EF-Tu
| EF-Tu | |||||||||
|---|---|---|---|---|---|---|---|---|---|
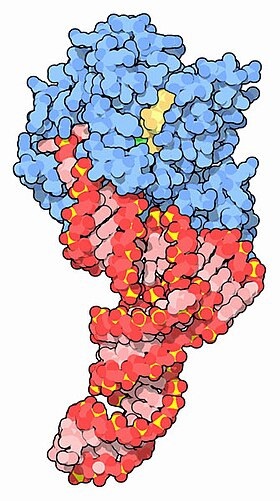 EF-Tu (青) と tRNA (赤)、GTP (黄) の複合体 [1] | |||||||||
| 識別子 | |||||||||
| 略号 | EF-Tu | ||||||||
| Pfam | GTP_EFTU | ||||||||
| InterPro | IPR004541 | ||||||||
| SCOP | 1ETU | ||||||||
| SUPERFAMILY | 1ETU | ||||||||
| |||||||||
EF-Tu(elongation factor thermo unstable)は、細菌の翻訳伸長因子であり、アミノアシルtRNA(アミノ酸が付加されたtRNA、aa-tRNA)のリボソームへの結合を触媒する。EF-TuはGタンパク質で、リボソームのA部位でのアミノアシルtRNAの選択と結合を促進する。その翻訳における重要性は、EF-Tuが細菌のタンパク質の中で、最も豊富に存在し、そして高度に保存されているものの1つであることからもうかがえる[2][3][4]。
背景
[編集]翻訳伸長因子は、リボソームでの翻訳によって新しいタンパク質を合成するメカニズムの一部である。
tRNAはタンパク質配列に組み込まれる個々のアミノ酸を運搬する。アミノアシルtRNAには、tRNAのアンチコドンに対応するアミノ酸が付加されている。mRNAはタンパク質の一次構造をコードする遺伝情報を保有しており、mRNA上の各コドンがアミノ酸を指定している。リボソームは、mRNAの情報に従ってaa-tRNAのアミノ酸をポリペプチド鎖に組み込んでいき、タンパク質の鎖を作りあげる[5][6]。
リボソームにはtRNAの結合部位が3つ存在する。A部位(aminoacyl/acceptor site)、P部位(peptidyl site)、そしてE部位(exit site)である。P部位には合成中のポリペプチド鎖に結合したtRNAが結合しており、A部位では、そこに位置するmRNAのコドンに相補的なアンチコドンを持つaa-tRNAの選別と結合が起こる。A部位でのaa-tRNAの結合の後、P部位のtRNAのポリペプチド鎖とA部位のtRNAのアミノ酸の間でペプチド結合が形成され、ポリペプチド鎖全体がP部位のtRNAからA部位のtRNAへ転移する。その後、細菌の翻訳伸長因子EF-G(歴史的には translocase として知られる)に触媒される形でtRNAとmRNAの協調的な移動(トランスロケーション)が起こり、P部位のtRNAがE部位へ移動してリボソームから解離し、A部位のtRNAが代わりにP部位へ移動する[5][6]。
生物学的機能
[編集]
タンパク質合成
[編集]EF-Tuはタンパク質合成のポリペプチドの伸長過程に関与する。細菌では、EF-Tuの主要な機能は正しいaa-tRNAをリボソームのA部位に運搬することである。EF-TuはGタンパク質であり、その機能には GTP が利用される。リボソーム外で、GTPを結合したEF-Tu(EF-Tu•GTP)がaa-tRNAと安定なEF-Tu•GTP•aa-tRNA三者複合体を形成する[7]。EF-Tu•GTPは、開始tRNAとセレノシステイン-tRNA を除く、全ての正しくアミノ酸が付加されたaa-tRNAとほぼ同じ親和性で結合する[8][9]。アミノ酸残基の性質はそれぞれ異なるが、側鎖の結合親和性の差を補償するさまざまな構造をtRNAは持っている[10][11]。
三者複合体はリボソームのA部位に移動し、tRNAのアンチコドンがmRNAのコドンと対合する。正しいアンチコドンがmRNAのコドンに対合している場合には、リボソームはその構成を変化させてEF-Tuの GTPアーゼドメインの形状を変化させる。その結果、EF-Tuに結合したGTPはGDPとリン酸に加水分解される。このように、リボソームはEF-Tuに対して GTPアーゼ活性化タンパク質(GAP)のような機能を果たす。GTPの加水分解に伴ってEF-Tuのコンフォメーションは劇的に変化し、aa-tRNAを解離してリボソームから出てゆく[4][12]。その後aa-tRNAはA部位に深く入り込み、そのアミノ酸部分はP部位のポリペプチドに近接する。そしてリボソームはP部位のポリペプチドからA部位のアミノ酸への共有結合の転移を触媒する[9]。
細胞質では、細菌の翻訳伸長因子EF-Tsによって、不活性化されたEF-Tu•GDPからGDPが取り除かれる。EF-TsがEF-Tuから解離すると、EF-TuはGTPと複合体を形成する。これは細胞質のGTPの濃度がGDPの濃度よりも5-10倍高いためである。このようにして再活性化されたEF-Tu•GTPは、再び別のaa-tRNAと三者複合体を形成する[7][12]。
翻訳の正確性の維持
[編集]EF-Tuは、3つの方法で翻訳の正確性に寄与する。翻訳における根本的な問題は、類似した(near-cognate)アンチコドンが正しい(cognate)アンチコドンと同等の親和性を持っているため、リボソームでのアンチコドン-コドン対合だけでは翻訳の正確性の高さを維持するには不十分である、ということである。これについては、A部位のtRNAがmRNAのコドンにマッチしないときには、リボソームがEF-TuのGTPアーゼ活性を活性化しないことで対処がなされている。これによって、不正確なtRNAがリボソームから出て行く可能性が高められている[13]。それに加え、EF-TuはtRNAのマッチに関係なく、aa-tRNAを解離してからaa-tRNAがA部位に完全に納まるまで(accommodationと呼ばれる過程)を遅らせる。この遅延期間は、正しくないアミノ酸がポリペプチド鎖に非可逆的に付加される前にaa-tRNAがA部位から出ていく2番目の機会となる[14][15]。3番目のメカニズムはあまり解明されていない機能で、EF-Tuはaa-tRNAを大雑把に検査し、アミノ酸がそれをコードする正しいtRNAに結合していない複合体をはじいている[10]。
他の機能
[編集]EF-Tuは細菌の細胞骨格にも多く見つかり、細胞の形状を維持する細胞骨格の要素であるMreBとともに細胞膜の直下に局在している[16][17]。EF-Tuの欠陥によって、細菌の形態に欠陥が生じることも示されている[18]。加えて、EF-Tuはシャペロンのような機能を示すことがあり、in vitroでは多くの変性タンパク質の再フォールディングを促進することを示唆する実験的なエビデンスが存在する[19][20]。
構造
[編集]
EF-Tu は単量体タンパク質で、大腸菌Escherichia coliでは分子量は約43kである[21][22][23]。タンパク質は、GTP結合ドメイン(ドメインI)と、オリゴヌクレオチド結合ドメイン(ドメインII、III)の3つの構造ドメインから構成される。N末端のドメインIは6本のα-ヘリックスに囲まれた6本のβ-ストランドのコアからなり[7]、ドメインIIとIIIは両方ともβ-バレル構造をとる[24][25]。
GTPを結合するドメインIはGTPのGDPへの加水分解によって劇的なコンフォメーション変化が起こり、それによってEF-Tuはaa-tRNAを解離してリボソームから出ていく[26]。EF-Tuの再活性化は細胞質でのGTPの結合によって行われ、再び大きなコンフォメーション変化によってEF-TuのtRNA結合部位が再活性化される。特に、EF-TuへのGTPの結合によって、ドメインIはドメインII、IIIに対して約90°回転し、tRNA結合の活性部位の残基が露出する[27]。
疾患との関連性
[編集]EF-Tuは、リボソームとともに、抗生物質による翻訳阻害の最も重要な標的の1つである[7]。EF-Tuを標的とする抗生物質は、その作用機序によって2つのグループに分類される。最初のグループはプルボマイシン(pulvomycin)と GE2270A を含むグループであり、EF-Tu•GTP•aa-tRNA三者複合体の形成を阻害する[28]。2番目のグループはキロマイシン(kirromycin)とenacyloxinを含むグループであり、GTPの加水分解後のリボソームからの解離を阻害する[29][30][31]。
出典
[編集]- ^ 蛋白質構造データバンク 今月の分子81:伸長因子(Elongation Factors)
- ^ “Elongation factor Tu: a molecular switch in protein biosynthesis”. Molecular Microbiology 6 (6): 683–8. (March 1992). doi:10.1111/j.1365-2958.1992.tb01516.x. PMID 1573997.
- ^ “NCBI CDD Conserved Protein Domain EF-Tu”. www.ncbi.nlm.nih.gov. 2018年12月9日閲覧。
- ^ a b “EF-G and EF4: translocation and back-translocation on the bacterial ribosome”. Nature Reviews. Microbiology 12 (2): 89–100. (February 2014). doi:10.1038/nrmicro3176. PMID 24362468.
- ^ a b “Initiation of protein synthesis in bacteria”. Microbiology and Molecular Biology Reviews 69 (1): 101–23. (March 2005). doi:10.1128/MMBR.69.1.101-123.2005. PMC 1082788. PMID 15755955.
- ^ a b “Ribosome structure and the mechanism of translation”. Cell 108 (4): 557–72. (February 2002). doi:10.1016/s0092-8674(02)00619-0. PMID 11909526.
- ^ a b c d “Mechanisms of EF-Tu, a pioneer GTPase”. Progress in Nucleic Acid Research and Molecular Biology 71: 513–51. (2002-01-01). PMID 12102560.
- ^ “Translation elongation factor EFTu/EF1A, bacterial/organelle (IPR004541) < InterPro < EMBL-EBI”. www.ebi.ac.uk. 2018年12月9日閲覧。
- ^ a b “Protein Synthesis Copyright © by Joyce J. Diwan. All rights reserved. Molecular Biochemistry II. - ppt download”. slideplayer.com. 2018年12月9日閲覧。
- ^ a b “Uniform binding of aminoacyl-tRNAs to elongation factor Tu by thermodynamic compensation”. Science 294 (5540): 165–8. (October 2001). doi:10.1126/science.1064242. PMID 11588263.
- ^ “Relative affinities of all Escherichia coli aminoacyl-tRNAs for elongation factor Tu-GTP”. The Journal of Biological Chemistry 259 (8): 5010–6. (April 1984). PMID 6370998.
- ^ a b “The ternary complex of EF-Tu and its role in protein biosynthesis”. Current Opinion in Structural Biology 7 (1): 110–6. (February 1997). doi:10.1016/s0959-440x(97)80014-0. PMID 9032056.
- ^ “Elongation factors on the ribosome”. Current Opinion in Structural Biology 15 (3): 349–54. (June 2005). doi:10.1016/j.sbi.2005.05.004. PMID 15922593.
- ^ “Accommodation of aminoacyl-tRNA into the ribosome involves reversible excursions along multiple pathways”. RNA 16 (6): 1196–204. (June 2010). doi:10.1261/rna.2035410. PMC 2874171. PMID 20427512.
- ^ “How EF-Tu can contribute to efficient proofreading of aa-tRNA by the ribosome”. Nature Communications 7: 13314. (October 2016). doi:10.1038/ncomms13314. PMC 5095583. PMID 27796304.
- ^ “Bacterial translation elongation factor EF-Tu interacts and colocalizes with actin-like MreB protein”. Proceedings of the National Academy of Sciences of the United States of America 107 (7): 3163–8. (February 2010). doi:10.1073/pnas.0911979107. PMC 2840354. PMID 20133608.
- ^ “Cytoskeletons in prokaryotes”. Cell Biology International 27 (5): 429–38. (2003-01-01). doi:10.1016/s1065-6995(03)00035-0. PMID 12758091.
- ^ “Cytoskeletal elements in bacteria Mycoplasma pneumoniae, Thermoanaerobacterium sp., and Escherichia coli as revealed by electron microscopy”. Journal of Molecular Microbiology and Biotechnology 11 (3-5): 228–43. (2006-01-01). doi:10.1159/000094057. PMID 16983198.
- ^ “Protein-disulfide isomerase activity of elongation factor EF-Tu”. Biochemical and Biophysical Research Communications 252 (1): 156–61. (November 1998). doi:10.1006/bbrc.1998.9591. PMID 9813162.
- ^ “Renaturation of rhodanese by translational elongation factor (EF) Tu. Protein refolding by EF-Tu flexing”. The Journal of Biological Chemistry 272 (51): 32206–10. (December 1997). doi:10.1074/jbc.272.51.32206. PMID 9405422.
- ^ “Purification of elongation factors EF-Tu and EF-G from Escherichia coli by covalent chromatography on thiol-sepharose”. Protein Expression and Purification 14 (1): 65–70. (October 1998). doi:10.1006/prep.1998.0922. PMID 9758752.
- ^ “Mapping Escherichia coli elongation factor Tu residues involved in binding of aminoacyl-tRNA”. The Journal of Biological Chemistry 271 (34): 20406–11. (August 1996). doi:10.1074/jbc.271.34.20406. PMID 8702777.
- ^ “Isolation of the protein synthesis elongation factors EF-Tu, EF-Ts, and EF-G from Escherichia coli”. Methods in Enzymology 60: 593–606. (1979-01-01). doi:10.1016/s0076-6879(79)60056-3. PMID 379535.
- ^ “Crystal structure of the EF-Tu.EF-Ts complex from Thermus thermophilus”. Nature Structural Biology 4 (8): 650–6. (August 1997). doi:10.1038/nsb0897-650. PMID 9253415.
- ^ “Crystal structure of the ternary complex of Phe-tRNAPhe, EF-Tu, and a GTP analog”. Science 270 (5241): 1464–72. (December 1995). doi:10.1126/science.270.5241.1464. PMID 7491491.
- ^ “A conserved amino acid sequence around Arg-68 of Artemia elongation factor 1 alpha is involved in the binding of guanine nucleotides and aminoacyl transfer RNAs”. Biochimie 69 (9): 983–9. (September 1987). doi:10.1016/0300-9084(87)90232-x. PMID 3126836.
- ^ “The crystal structure of elongation factor EF-Tu from Thermus aquaticus in the GTP conformation”. Structure 1 (1): 35–50. (September 1993). PMID 8069622.
- ^ “Antibiotic GE2270 a: a novel inhibitor of bacterial protein synthesis. I. Isolation and characterization”. The Journal of Antibiotics 44 (7): 693–701. (July 1991). doi:10.7164/antibiotics.44.693. PMID 1908853.
- ^ “Inhibitory mechanisms of antibiotics targeting elongation factor Tu”. Current Protein & Peptide Science 3 (1): 121–31. (February 2002). doi:10.2174/1389203023380855. PMID 12370016.
- ^ “Elongation factors in protein biosynthesis”. Trends in Biochemical Sciences 28 (8): 434–41. (August 2003). doi:10.1016/S0968-0004(03)00162-2. PMID 12932732.
- ^ “Elongation factor Tu-targeted antibiotics: four different structures, two mechanisms of action”. FEBS Letters 580 (19): 4576–81. (August 2006). doi:10.1016/j.febslet.2006.07.039. PMID 16876786.
関連項目
[編集]- 翻訳伸長因子
- EF-Ts (elongation factor thermo stable)
- EF-G (elongation factor G)
- EF-P (elongation factor P)
- eEF1(eukaryotic elongation factor 1)
- EFR(EF-Tu receptor)


 French
French Deutsch
Deutsch